Une équipe internationale a développé l'arbre généalogique des oiseaux le plus complet, couvrant 93 millions d'années et 92 % des familles d'oiseaux, en utilisant des méthodes informatiques avancées et des ressources de calcul intensif. Crédit : Issues.fr.com
Une équipe mondiale de chercheurs a construit l'arbre généalogique des oiseaux le plus complet et le plus étendu à ce jour, détaillant les liens évolutifs entre 363 oiseaux. espèces sur 93 millions d'années. Ce graphique représente 92% de toutes les familles d'oiseaux.
Cette avancée a été rendue possible en grande partie grâce aux méthodes informatiques de pointe développées par des ingénieurs de l'Université de Californie à San Diego, combinées aux ressources de superinformatique de pointe de l'université au San Diego Supercomputer Center. Ces technologies ont permis aux chercheurs d'analyser de grandes quantités de données génomiques avec une grande précision. précision et rapidité, jetant les bases de la construction de l'arbre généalogique des oiseaux le plus complet jamais assemblé.
L'avancée est détaillée dans deux articles complémentaires publiés le 1er avril dans Nature et le Actes de l'Académie nationale des sciences (PNAS). L'arbre généalogique mis à jour, rapporté dans Naturea révélé des modèles dans l'histoire évolutive des oiseaux à la suite de l'extinction massive cataclysmique qui a anéanti les dinosaures il y a 66 millions d'années.
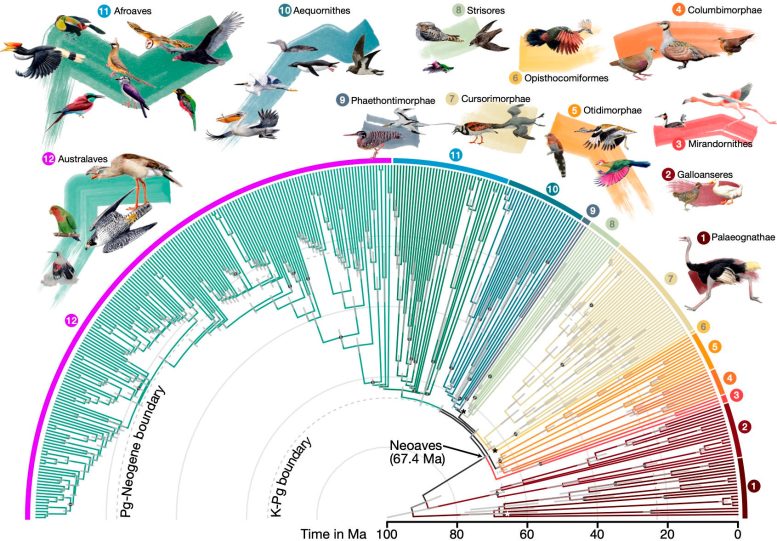
L'arbre généalogique des oiseaux mis à jour, publié dans Nature, délimitant 93 millions d'années de relations évolutives entre 363 espèces d'oiseaux. Crédits : Jon Fjeldså (dessins) et Josefin Stiller
Les chercheurs ont observé une forte augmentation de la taille effective de la population, des taux de substitution et de la taille relative du cerveau chez les lève-tôt, apportant ainsi un nouvel éclairage sur les mécanismes adaptatifs qui ont conduit à la diversification aviaire à la suite de cet événement crucial. Dans l'article complémentaire publié dans PNASles chercheurs ont examiné de près l'une des branches du nouvel arbre généalogique et ont découvert que les flamants roses et les tourterelles sont plus éloignés que ne l'avaient montré les analyses précédentes à l'échelle du génome.
Le travail fait partie du projet Bird 10 000 Genomes (B10K), un effort multi-institutionnel dirigé par l'Université de Copenhague, l'Université du Zhejiang et l'UC San Diego qui vise à générer des projets de séquences génomiques pour environ 10 500 espèces d'oiseaux existantes.
« Notre objectif est de reconstruire toute l'histoire évolutive de tous les oiseaux », a déclaré Siavash Mirarab, professeur de génie électrique et informatique à la Jacobs School of Engineering de l'UC San Diego, qui est co-auteur principal de l'étude. Nature article, ainsi que premier auteur et co-correspondant sur le PNAS papier.
Reconstituer le passé
Au cœur de ces études se trouve une suite d'algorithmes connus sous le nom d'ASTRAL, que le laboratoire de Mirarab a développés pour déduire des relations évolutives avec une évolutivité, une précision et une rapidité sans précédent. En exploitant la puissance de ces algorithmes, l’équipe a intégré les données génomiques de plus de 60 000 régions génomiques, fournissant ainsi une base statistique solide pour leurs analyses.
Les chercheurs ont ensuite examiné l’histoire évolutive de segments individuels du génome. À partir de là, ils ont reconstitué une mosaïque d’arbres génétiques, qui ont ensuite été compilés en un arbre d’espèces complet. Cette approche méticuleuse a permis aux chercheurs de construire un nouvel arbre généalogique des oiseaux amélioré qui délimite des événements de ramification complexes avec une précision et des détails remarquables, même en cas d'incertitude historique.
« Nous avons découvert que notre méthode consistant à ajouter des dizaines de milliers de gènes à notre analyse était en réalité nécessaire pour résoudre les relations évolutives entre les espèces d'oiseaux », a déclaré Mirarab. « Vous avez vraiment besoin de toutes ces données génomiques pour récupérer avec une grande confiance ce qui s'est passé au cours de cette certaine période il y a 65 à 67 millions d'années. »

Dans l'étude publiée dans PNAS, les chercheurs ont examiné de près l'une des branches de l'arbre généalogique des oiseaux mis à jour et ont découvert que les groupes comprenant les flamants roses et les tourterelles sont plus éloignés que les analyses précédentes à l'échelle du génome ne l'avaient montré et ont attribué le résultat à une région inhabituelle du chromosome. 4. Crédit : Ed Braun (dessins), Daniel J. Field (images d'oiseaux) et Siavash Miarab
La capacité de l'équipe à effectuer ces analyses sur des ensembles de données massifs a été rendue possible parce que le laboratoire de Mirarab a conçu ses méthodes de calcul pour qu'elles fonctionnent sur de puissantes machines GPU. Ils ont effectué leurs calculs sur Étendue supercalculateur au supercalculateur de San Diego à l'UC San Diego.
« Nous avons eu la chance d'avoir accès à un supercalculateur aussi haut de gamme », a déclaré Mirarab. « Sans Étenduenous n’aurions pas pu exécuter et réexécuter nos analyses sur des ensembles de données aussi volumineux dans un délai raisonnable.
Les chercheurs ont également examiné les effets de différentes méthodes d’échantillonnage du génome sur la précision de l’arbre. Ils ont montré que deux stratégies – le séquençage de nombreux gènes de chaque espèce, ainsi que le séquençage de nombreuses espèces – combinées sont importantes pour reconstruire cette histoire évolutive.
« Comme nous avons utilisé un mélange des deux stratégies, nous avons pu tester quelle approche avait le plus fort impact sur la reconstruction phylogénétique », a déclaré Josefin Stiller, professeur de biologie à l'Université de Copenhague et auteur principal de l'étude. Nature papier. « Nous avons constaté qu'il était plus important d'échantillonner de nombreuses séquences génétiques de chaque organisme que d'échantillonner un plus large éventail d'espèces, bien que cette dernière méthode nous ait aidé à dater l'évolution de différents groupes. »
Corriger le passé
Grâce à leurs méthodes informatiques avancées, les chercheurs ont également pu faire la lumière sur quelque chose d'inhabituel qu'ils avaient découvert lors d'une de leurs études précédentes : une section particulière d'un chromosome dans le génome de l'oiseau était restée inchangée pendant des millions d'années, vide des modèles attendus de recombinaison génétique.
Cette anomalie a initialement conduit les chercheurs à regrouper de manière incorrecte les flamants roses et les colombes en tant que cousins évolutifs, car ils semblaient étroitement liés sur la base de cette section inchangée de ADN. C’est parce que leur analyse précédente était basée sur les génomes de 48 espèces d’oiseaux. Mais en répétant leur analyse en utilisant les génomes de 363 espèces, un arbre généalogique plus précis a émergé, éloignant les tourterelles des flamants roses. De plus, en utilisant six génomes de haute qualité fournis par le Vertebrate Genome Project (VGP) – dirigé par le co-auteur Erich Jarvis, professeur de neurobiologie à l’Université Rockefeller – Mirarab et ses collègues ont pu détecter et expliquer ce schéma surprenant.
« Ce qui est surprenant, c'est que cette période de recombinaison supprimée puisse induire l'analyse en erreur », a déclaré Edward Braun, professeur de biologie à l'Université de New York. Université de Floride et auteur co-correspondant du PNAS papier. « Et parce que cela pouvait induire l’analyse en erreur, il était en fait détectable plus de 60 millions d’années dans le futur. C'est ce qui est cool.
Prochaines étapes
L’impact de ces travaux s’étend bien au-delà de l’étude de l’histoire évolutive des oiseaux. Les méthodes informatiques mises au point par le laboratoire de Mirarab sont devenues l'un des outils standards pour reconstruire les arbres évolutifs d'une variété d'autres animaux.
À l’avenir, l’équipe poursuit ses efforts pour construire une image complète de l’évolution des oiseaux. Les biologistes travaillent au séquençage des génomes d’autres espèces d’oiseaux dans l’espoir d’élargir l’arbre généalogique pour inclure des milliers de genres d’oiseaux. Pendant ce temps, les informaticiens dirigés par Mirarab affinent leurs algorithmes pour s'adapter à des ensembles de données encore plus volumineux afin de garantir que les analyses des études futures soient effectuées avec une rapidité et une précision élevées.




