Un projet révolutionnaire a cartographié l'ADN de plus de 9 500 plantes à fleurs, fournissant ainsi de nouvelles informations sur l'évolution des plantes et rendant les données librement disponibles pour la recherche sur la biodiversité et d'autres domaines scientifiques. Crédit : Issues.fr.com
L'arbre de vie des plantes à fleurs, tout comme notre propre arbre généalogique, nous permet de comprendre à quel point espèces sont liés les uns aux autres. L'arbre de vie se révèle en comparant ADN séquences entre différentes espèces pour identifier les changements (mutations) qui s’accumulent au fil du temps comme un enregistrement fossile moléculaire. Notre compréhension de l’arbre de vie s’améliore rapidement grâce aux progrès de la technologie de séquençage de l’ADN.
Un vaste arbre de vie ADN apporte des séquences d'ADN en libre accès de plus de 9 500 plantes à fleurs a été récemment réalisé par des scientifiques des jardins botaniques royaux de Kew, en collaboration avec des collaborateurs de l'Institut de botanique de Kunming (KIB) de l'Académie chinoise des sciences et des environs. Dans le monde entier, cette ressource inestimable nous permet de répondre à des questions clés sur la vie végétale moderne et de remonter le temps jusqu'à ses origines. Leur étude a été récemment publiée dans Nature.
Avancées technologiques dans le séquençage de l'ADN
L’un des principaux avantages de cette approche est qu’elle peut être utilisée pour séquencer une large gamme de matériel végétal, ancien et nouveau, même lorsque l’ADN est gravement endommagé. Les vastes trésors de matériel végétal séché des collections d'herbiers du monde, qui comprennent près de 400 millions de spécimens scientifiques de plantes, peuvent désormais être étudiés génétiquement.
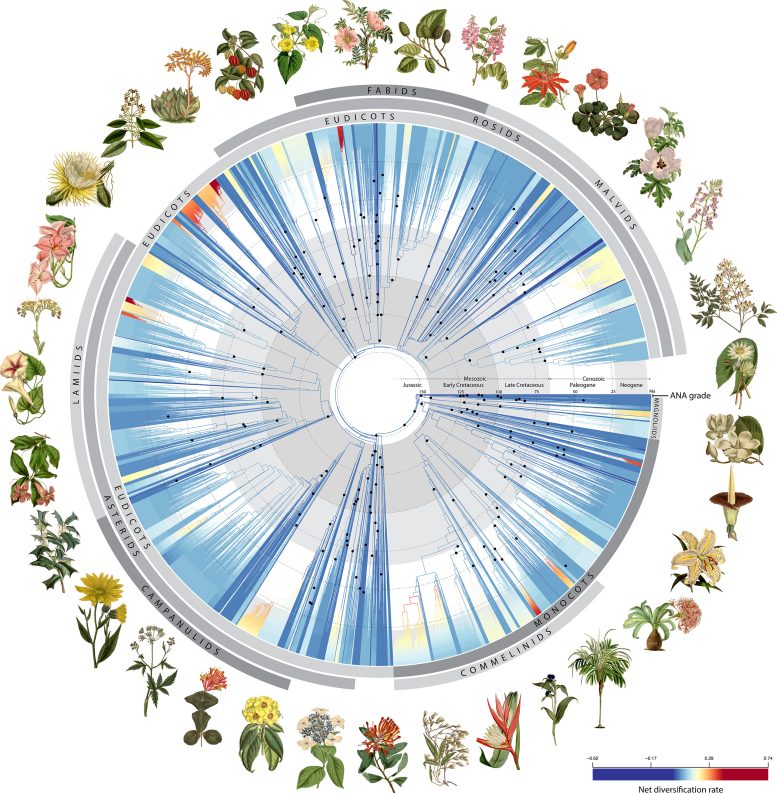
Arbre de vie angiosperme. Crédit : RBG Kew
À l’aide de tels spécimens, les chercheurs ont séquencé un spécimen de sandwort (Arenaria globiflora) collectés il y a près de 200 ans au Népal et, malgré la mauvaise qualité de son ADN, ont pu le placer dans l'arbre de vie. Ils ont même analysé des plantes disparues, comme l'olivier de l'île Guadalupe (Hesperelaea palmeri), qui n'a pas été observée vivante depuis 1875. En fait, 511 des espèces séquencées sont déjà menacées d'extinction, selon la Liste rouge de l'Union internationale pour la conservation de la nature, dont trois autres Hespérée qui sont déjà éteints.
Collaboration mondiale et nouvelles découvertes
Sur les 9 506 espèces séquencées pour cette étude, plus de 3 400 provenaient de matériel provenant de 163 herbiers dans 48 pays, avec du matériel supplémentaire provenant de collections de plantes du monde entier (par exemple, banques d'ADN, graines et collections vivantes).
Parmi les espèces séquencées, plus de 800 n’avaient jamais vu leur ADN séquencé auparavant. Ce séquençage était essentiel pour combler d’importantes lacunes dans les connaissances et apporter un nouvel éclairage sur l’histoire évolutive des plantes à fleurs. Les chercheurs ont également bénéficié de données accessibles au public sur plus de 1 900 espèces, soulignant la valeur de l’approche scientifique ouverte pour la future recherche génomique.
Malgré les propriétés biologiques contrastées des génomes nucléaire et plastidique (par exemple, taille, nombre de copies, mode d'hérédité, recombinaison et taux d'évolution), qui peuvent conduire à des arbres phylogéniques contradictoires, les résultats soutiennent largement la classification phylogénétique principalement basée sur les plastes. le groupe de phylogénie des angiospermes IV. Par exemple, 58 des 64 commandes actuellement acceptées et 406 des 416 familles ont été récupérées comme monophylétiques (hors artefacts).
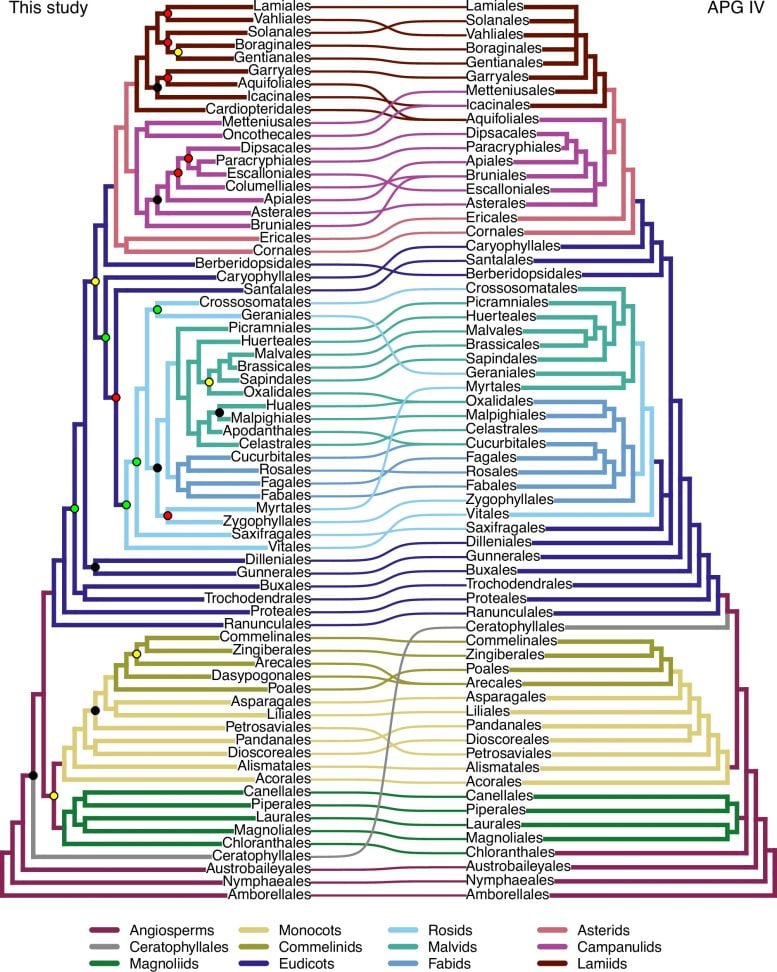
Tanglegram au niveau ordinal entre ce travail (à gauche) et l'arbre schématique APG IV (à droite). Crédit : KIB
L’exception la plus frappante est la non-monophylie des Astéracées, la plus grande famille d’angiospermes, qui comprend les tournesols et leurs proches. L'arbre produit par cette étude confirme également 85% des relations entre familles récupérées par l'arbre phylogénomique des angiospermes à l'aide de plastomes par les scientifiques du KIB.
Le « mystère abominable » de Darwin et ses idées évolutionnistes
Les plantes à fleurs sont apparues il y a plus de 140 millions d’années, après quoi elles ont rapidement dépassé les autres plantes vasculaires. Darwin fut intrigué par l’apparition apparemment soudaine d’une telle diversité dans les archives fossiles et écrivit : « Le développement rapide, autant que nous puissions en juger, de toutes les plantes supérieures au cours des temps géologiques récents est un abominable mystère. »
À l’aide de 200 fossiles, les chercheurs ont retracé leur arbre de vie dans le temps pour montrer comment les plantes à fleurs ont évolué au fil des temps géologiques. Ils ont découvert que la diversité des plantes à floraison précoce explosait effectivement, comme l'a noté Darwin. Le développement rapide de ces plantes a donné naissance, peu après leur origine, à plus de 80 % des grandes lignées existantes. Cependant, cette tendance a ensuite diminué jusqu'à atteindre un rythme plus stable au cours des 100 millions d'années suivantes, jusqu'à ce qu'une nouvelle poussée de diversification se produise il y a environ 40 millions d'années, coïncidant avec une baisse mondiale de la température.
Ces nouvelles découvertes auraient fasciné Darwin et aideront sûrement les scientifiques d'aujourd'hui à relever le défi de comprendre comment et pourquoi les espèces se diversifient.
L’arbre de vie, une plante à fleurs, présente un énorme potentiel pour la recherche sur la biodiversité. En effet, tout comme on peut prédire les propriétés d’un élément en fonction de sa position dans le tableau périodique, la localisation d’une espèce dans l’arbre de vie permet de prédire ses propriétés. Les nouvelles données seront donc inestimables pour améliorer de nombreux domaines scientifiques et au-delà.
Pour rendre cela possible, l'arbre et toutes ses données sous-jacentes ont été mis à la disposition du public et de la communauté scientifique de manière ouverte et gratuite, notamment via le Kew Tree of Life Explorer. Les chercheurs estiment qu’un tel libre accès est essentiel pour démocratiser l’accès aux données scientifiques dans le monde.
Le libre accès aidera également les scientifiques à tirer le meilleur parti des données, par exemple en les combinant avec l’intelligence artificielle pour prédire quelles espèces végétales peuvent contenir des molécules au potentiel médicinal. De la même manière, l’arbre de vie peut être utilisé pour mieux comprendre et prédire comment les ravageurs et les maladies affecteront les plantes à l’avenir. En fin de compte, notent les chercheurs, les applications de ces données dépendront de l’ingéniosité des scientifiques qui y accéderont.




