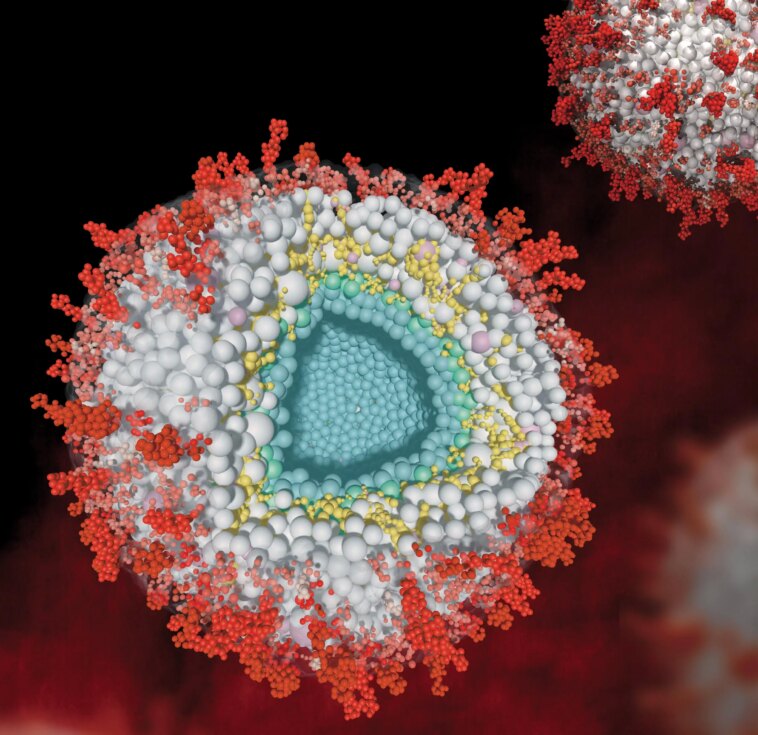
Modèle de virions de l’herpèsvirus en coupe transversale (au centre) et non coupé (en haut à droite). En surface, des glycoprotéines virales (rouges) sont intégrées dans une membrane (transparente). La membrane renferme diverses protéines virales du tégument (gris) et des protéines assimilées de l’hôte (rose). La protéine du tégument viral UL32 est surlignée en jaune. Au centre du virion se trouve l’ADN (non représenté) qui est entouré par la nucléocapside (bleue). Crédit : Yueheng Zhou, Absea Biotechnology
Les virus de l’herpès sont traîtres : une fois qu’ils vous infectent, ils restent avec vous pour la vie. Cela est dû à leur capacité à rester en sommeil dans certaines cellules du corps. Presque chaque adulte héberge sans le savoir au moins un des neuf virus de l’herpès humain distincts. Des facteurs comme l’âge, le stress ou un système immunitaire affaibli peuvent réactiver la virusentraînant des maladies potentiellement graves.
Les virus de l’herpès connaissent un tel succès en raison de leur remarquable adaptation à l’homme et de leurs stratégies pour échapper à notre système immunitaire. La clé de leur déguisement réside dans des protéines qui trompent la cellule infectée en lui faisant croire qu’elle n’est pas menacée. On sait par exemple que tout virus de l’herpès possède un protéome puissant, c’est-à-dire un grand nombre de ces protéines, qui, très adapté à l’hôte, lui permet de se répliquer efficacement immédiatement après l’infection.
Le protéome complexe garantit également que des particules multicouches sont accumulées dans la cellule déjà infectée. Ces virus nouvellement formés – également appelés virions – contiennent de nombreuses protéines virales ainsi que des protéines hôtes. Au centre des particules se trouve le virus ADN, qui est entourée d’une nucléocapside. Une couche de nombreuses autres protéines appelées téguments se forme autour de cette capside.
Les particules entrent en jeu dans la réactivation du virus
Les particules sont cruciales pour permettre au virus de se répliquer à nouveau et de se propager de manière systémique dans le corps après une réactivation déclenchée par quelque moyen que ce soit. Ils sont donc au cœur de l’apparition de la maladie – après une longue période de dormance (latence).
Cependant, on sait peu de choses sur l’organisation interne de ces particules, en particulier sur les interactions protéine-protéine au sein du tégument. Des chercheurs du Leibniz-Forschungsinstitut für Molekulare Pharmakologie (FMP) et de la Charité–Universitätsmedizin Berlin a donc examiné de plus près les particules, en particulier dans le cytomégalovirus humain (HCMV).
Le HCMV survient particulièrement fréquemment dans la population et peut être très dangereux, en particulier pour les receveurs de greffe et les enfants à naître qui sont infectés par la mère. Malgré des recherches intensives, il n’existe actuellement aucune thérapie antivirale bien tolérée qui pourrait contrôler efficacement ou même éliminer le virus. Il n’y a pas non plus de vaccination contre ce type de virus.
La carte montre quelles protéines interagissent les unes avec les autres
Dans les travaux en cours, l’équipe dirigée par Fan Liu (FMP) et Lüder Wiebusch (Charité) a pour la première fois créé une carte détaillée des interactions spatiales entre les protéines virales et de la cellule hôte au sein des particules de HCMV. Cela a révélé, entre autres, que certaines protéines de la cellule hôte sont recrutées par des protéines virales et jouent un rôle dans la réplication virale. Par exemple, une protéine virale appelée UL32 recrute une protéine cellulaire (protéine phosphatase, PP1) dans la particule pour éviter la liaison d’autres protéines indésirables de la cellule hôte.
« Le HCMV lui-même n’a pas de phosphatases comme PP1, vous pouvez donc voir que le virus profite de certaines protéines de la cellule hôte pour se répliquer efficacement », explique le virologue FMP Boris Bogdanow, expliquant une stratégie clé pour la façon dont le HCMV trompe son hôte.
Pour étudier les interactions entre les différentes protéines dans les particules intactes de HCMV couche par couche, les chercheurs ont utilisé une technique appelée spectrométrie de masse réticulée. « Cette méthode nous permet aussi de tirer des conclusions sur l’identité des protéines », souligne Fan Liu, expert en spectrométrie de masse au FMP. « Mais ce qui est spécial et unique dans la réticulation, c’est que nous pouvons voir quelles protéines interagissent les unes avec les autres et où. »
Jamais auparavant cette technologie innovante n’avait été utilisée pour cartographier l’organisation spatiale des interactions au sein des particules d’herpèsvirus. Avec les données ainsi obtenues, un modèle informatique de la particule HCMV a ensuite été créé au FU Berlin par Mohsen Sadeghi. Le modèle virtuel permet la simulation de chaque protéine dans la particule et visualise les processus biophysiques de manière vivante.
« L’interaction protéine-protéine identifiée est importante pour mieux comprendre le cycle de vie complexe du HCMV », classe Boris Bogdanow. « Et ceci, à son tour, est important pour trouver des médicaments antiviraux candidats contre le HCMV. »