Une étude révolutionnaire utilisant des données à l’échelle génomique complète a révolutionné notre compréhension de l’évolution des oiseaux, révélant de nouvelles informations sur les relations phylogénétiques entre les espèces d’oiseaux. En analysant un ensemble de données complet de 363 espèces d'oiseaux, la recherche a redéfini l'arbre généalogique aviaire, identifiant quatre clades majeurs au sein des Neoaves et mettant en lumière l'histoire évolutive complexe des oiseaux. Crédit : Issues.fr.com
L’étude génomique la plus approfondie à ce jour a révélé comment les oiseaux se sont répandus dans le monde entier après une extinction massive.
Les oiseaux représentent la seule lignée de dinosaures survivante de nos jours. Il y a environ 66 millions d'années, à la transition du Crétacé À la période paléogène (la limite K – Pg), un événement d'extinction catastrophique a conduit à la disparition de tous les dinosaures non aviaires, offrant ainsi aux oiseaux la possibilité de se diversifier rapidement et d'occuper un large éventail de niches écologiques.
Neoaves, un groupe diversifié comprenant environ 95 % de tous les oiseaux espèces aujourd'hui, est née de ce rayonnement. Des imposants condors des Andes aux petits colibris volant à travers les forêts tropicales, les Neoaves englobent une étonnante diversité de formes et de fonctions.
Malgré des efforts considérables pour reconstruire l'histoire évolutive des oiseaux et les impacts de l'événement K-Pg à l'aide de données morphologiques et moléculaires, l'ordre précis des ramifications et les relations entre les lignées néoaviennes sont restés controversés.
« Des études antérieures sur de petits ensembles de données provenant de différentes régions génomiques ont souvent produit des résultats contradictoires en ce qui concerne la topologie de l'arbre à oiseaux », a déclaré Guojie Zhang, auteur principal de l'article, professeur titulaire de la chaire de biologie évolutive à l'Université du Zhejiang et l'un des initiateurs de l'étude. le projet B10K. « Dans cette étude, pour la première fois, nous avons utilisé des données complètes à l'échelle du génome pour construire l'arbre des espèces d'oiseaux de presque toutes les familles représentatives. »
Avancées dans les données génomiques
Cet ensemble de données génomiques complet a été produit par le consortium B10K dans sa deuxième phase qui comprend 363 espèces d'oiseaux couvrant toutes les principales lignées d'oiseaux.
Le nouvel arbre généalogique innove dans le long voyage visant à percer les mystères de l'évolution des oiseaux. Selon cet arbre généalogique d'oiseaux mis à jour, un groupe contenant des flamants roses et des grèbes (appelés Mirandornithes) a été parmi les premières lignées néoaviennes à évoluer.
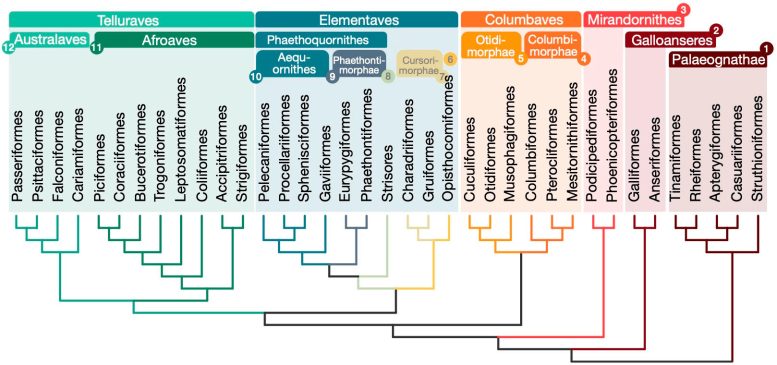
Relations pour 363 espèces d'oiseaux basées sur 63 430 loci intergéniques. Crédit : Josefin Stiller
Le nouvel arbre remet en question l'organisation des Néoaves en classant ce grand groupe en quatre clades majeurs : Mirandornithes, Columbaves, Elementaves et Telluraves. Elementaves est un groupe nouvellement proposé comprenant env. 14 % de toutes les espèces d'oiseaux modernes, y compris des groupes disparates tels que l'énigmatique hoatzin, les oiseaux de rivage, les colibris et les oiseaux tropiques.
Elementaves doit son nom à la remarquable diversité du groupe dans les niches écologiques, représentant les principaux éléments que sont la Terre, l'air et l'eau. Ce nouvel arbre généalogique résout certains débats de longue date sur les relations entre les espèces aviaires et établit une base solide pour l'étude de l'évolution et du développement des traits aviaires.
L'impact de l'analyse génomique complète
En utilisant des données génomiques complètes sur 363 espèces d’oiseaux, il s’agit du plus grand ensemble de données jamais utilisé pour les analyses phylogénétiques des oiseaux. L’équipe a construit un nouveau pipeline pour extraire plus de 150 000 régions réparties dans le génome.
« Nous avons caractérisé les relations phylogénétiques à travers l'ensemble du génome et identifié des modèles associés au contexte génomique et aux caractéristiques des séquences », a déclaré Josefin Stiller, auteur principal de cette étude et professeur adjoint en biologie évolutive à l'Université de Copenhague. « Nous avons constaté que divers des parties du génome, par exemple des chromosomes individuels ou des gènes codant pour des protéines, abritent souvent des arbres très différents. Cela explique probablement pourquoi les études qui analysaient uniquement certaines parties du génome étaient en conflit.
Rassembler de grandes quantités de données de haute qualité était essentiel pour produire un arbre phylogénétique robuste. L’équipe a découvert que pour la plupart des succursales, un consensus sur leurs relations peut être atteint lorsqu’une quantité suffisante de données est utilisée. Mais les positions phylogénétiques de certains groupes d’oiseaux comme les hiboux et les faucons restent déroutantes, même avec des données à l’échelle du génome complet.
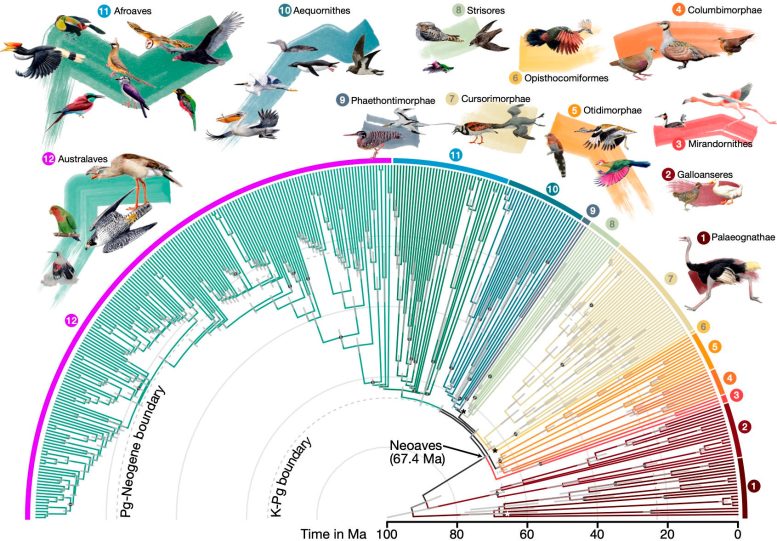
Temps de divergence pour 363 espèces d’oiseaux basés sur 63 430 loci intergéniques. Crédit : Josefin Stiller
« Plus de données ne produisent pas nécessairement une meilleure solution », a déclaré Zhang. Siavash Mirarab, co-auteur principal de l'étude et professeur de génie électrique et informatique à l'Université de Californie à San Diego, a ajouté que « la raison en est peut-être une histoire évolutive complexe comme un ancien croisement entre deux lignées ». tri incomplet des lignées, attraction des longues branches et biais ADN contenu de la séquence, qui peuvent tous interférer avec la reconstruction des arbres phylogénétiques.
L'étude rapporte de nouvelles informations sur lesquels de ces facteurs ont un impact sur quelles branches de l'arbre, fournissant ainsi une image plus complète et plus authentique de l'origine de ces groupes aviaires. L'étude propose également une échelle de temps plus précise pour la diversification des oiseaux modernes, suggérant qu'une radiation rapide s'est produite au moment ou à proximité de l'extinction massive à la limite Crétacé-Paléogène (K-Pg) et, dans une moindre mesure, peu de temps après le Paléogène-Néogène. frontière.
Les chercheurs ont découvert que ces radiations coïncidaient avec des changements génétiques et morphologiques remarquables chez les oiseaux, notamment des taux de mutation plus élevés, des corps plus petits, des cerveaux plus gros et des populations effectives plus grandes. « Cela illustre la puissance de la génomique comparative : en comparant les génomes d'espèces vivantes, nous pouvons découvrir des traces d'événements survenus il y a 66 millions d'années », a déclaré Stiller.
« Notre travail a modifié de nombreuses visions traditionnelles de l’histoire évolutive des oiseaux. Ce nouvel arbre généalogique servira de base solide pour cartographier l’histoire évolutive de toutes les espèces d’oiseaux, avec des implications importantes pour la recherche ornithologique et les études sur la biodiversité », a conclu Zhang.




